BiomedParse
BiomedParse 是一款专为生物医学图像分析打造的通用基础模型,能够跨九种成像模态(如 CT、MRI、病理切片等)统一执行分割、检测与识别任务。它有效解决了传统工具往往只能处理单一模态或特定任务的局限,帮助研究人员从复杂多样的医疗影像中高效提取关键信息,大幅降低多任务分析的门槛。
该工具特别适合生物医学领域的研究人员、临床医生及 AI 开发者使用,尤其是那些需要处理大规模、多模态影像数据的专业团队。BiomedParse 的最新 v2 版本引入了独特的 BoltzFormer 架构,显著提升了微小目标的分割精度,并支持端到端的 3D 体积推理,在相关国际挑战赛中荣获榜首。此外,它还内置了对象存在性检测模块,能自动过滤误报,无需额外的后处理步骤。无论是进行科研探索还是开发辅助诊断应用,BiomedParse 都提供了一个灵活且强大的技术基座。
使用场景
某三甲医院影像科团队正致力于构建一套自动化系统,用于从海量 3D CT 和 MRI 扫描数据中精准定位并识别微小肿瘤病灶及周围解剖结构。
没有 BiomedParse 时
- 多模型堆砌繁琐:研究人员需分别训练分割、检测和分类三个独立模型,代码维护复杂且推理流程冗长。
- 微小病灶漏检率高:传统架构难以捕捉 3D 体积数据中的细微特征,导致早期微小结节经常被忽略或误判。
- 假阳性过滤困难:模型常将正常组织误识别为病灶,后续必须编写额外的脚本进行统计检验(如 K-S 检验)来剔除假阳性结果。
- 3D 推理效率低下:缺乏端到端的体积推断能力,往往需要将 3D 数据切片处理后再重组,不仅耗时还容易丢失空间上下文信息。
使用 BiomedParse 后
- 统一架构高效集成:BiomedParse 单个模型即可同时完成分割、检测和识别任务,大幅简化了部署流程并提升了开发效率。
- 小目标检测显著提升:得益于内置的 BoltzFormer 架构,BiomedParse 能精准捕捉微小病灶,显著降低了漏检率。
- 内置假阳性抑制:利用其独有的 ISD 模块,BiomedParse 在推理阶段自动判断物体是否存在,无需额外后处理即可有效过滤误报。
- 原生 3D 端到端推断:BiomedParse 支持直接对 3D volumetric 数据进行推理,完整保留空间结构信息,将分析速度提升至秒级。
BiomedParse 通过统一的 foundation model 架构,彻底解决了多模态 3D biomedical 图像分析中流程割裂、小目标难识别及假阳性高的核心痛点。
运行环境要求
- Linux
需要 NVIDIA GPU (CUDA 12.4),支持端到端 3D 推理,显存需求未明确说明(建议大显存以处理 3D 体积数据)
未说明
快速开始
BiomedParse
【通知】这是 BiomedParse 模型的 v2 版本,采用了基于 BoltzFormer 的改进代码和模型架构,支持端到端的 3D 推理。如果您需要原始版本,请查看 v1。
本仓库托管了 BiomedParse 的代码与资源,即“用于跨九种模态的生物医学对象联合分割、检测与识别的基础模型”(Nature Methods)。BiomedParse 专为全面的生物医学图像分析而设计。它提供了一种统一的方法,可在多种生物医学成像模态中执行 分割、检测 和 识别 任务。通过整合这些任务,BiomedParse 为研究人员和从业者提供了一款高效且灵活的工具,有助于解析和分析复杂的生物医学数据。
v2 有哪些新特性?
自 BiomedParse 发表以来,我们不断收集社区反馈,并持续努力提升其功能与易用性。v2 版本提供了:
- 更大规模的
预训练数据,数量达百万级,涵盖不同模态下的 200 多个解剖结构。 - 使用
BoltzFormer架构,显著提升了小物体的分割性能。 - 实现了 SOTA 级别的 3D 分割性能,支持端到端的体素级推理(
CVPR 挑战赛)。 - 内置目标存在性检测功能,可有效减少假阳性(无需额外的掩码检查)。
我应该使用 v1 还是 v2?
简短回答:对于 3D 模态请使用 v2,其他情况则使用 v1。
| 版本 | 图像类型 | 模态 | 任务数量 | 存在性检测 |
|---|---|---|---|---|
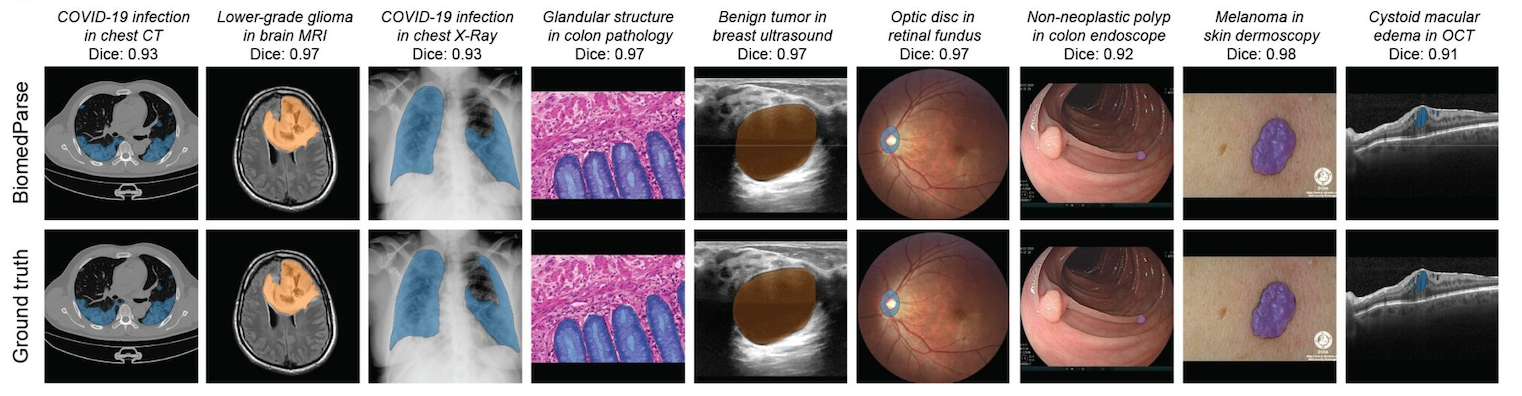
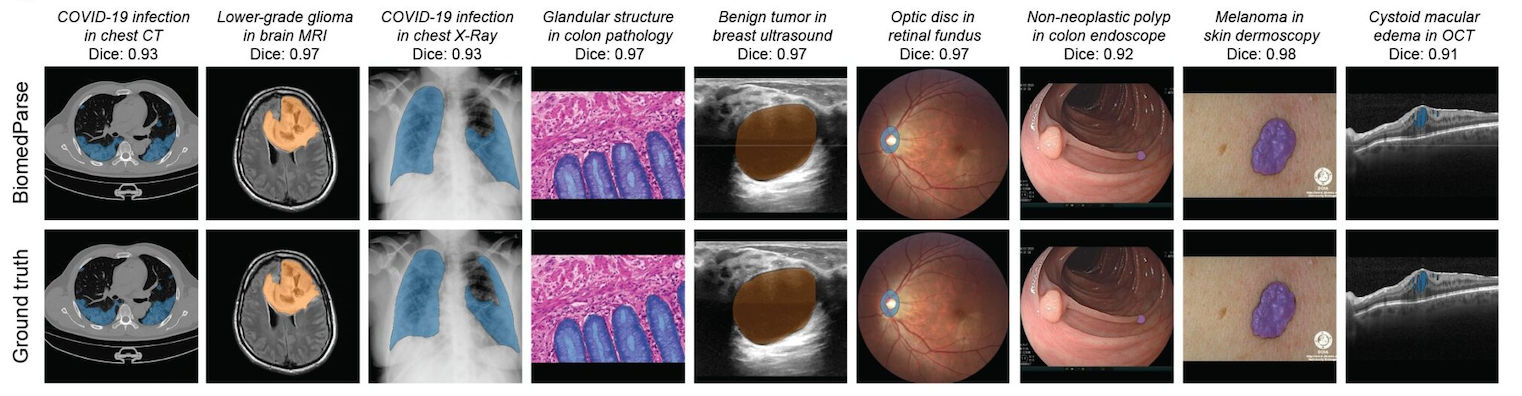
| v1 | 2D | CT、MRI、超声、X 射线、病理学、内窥镜、皮肤镜、眼底照相、OCT | 100+ | 推理后 K-S 检验 |
| v2 | 3D | CT、MRI、超声、PET、3D 显微镜(EM、光片显微镜) | 200+ | 内置 ISD 模块 |
最新动态
- 2025 年 10 月 15 日:BiomedParse v2 正式发布,全面支持推理与微调!
- 2025 年 6 月 11 日:BiomedParse 在
CVPR 2025: 文本引导的 3D 生物医学图像分割基础模型挑战赛中荣获第一名!我们升级了模型,并基于该挑战赛的数据集进行了微调,覆盖范围更广、更全面的 3D 生物医学影像数据。您可以通过容器化的 [docker 镜像] 直接进行推理。使用此版本模型时,请务必注明原挑战赛来源。 - 2025 年 1 月 9 日:优化了所有目标识别脚本,并新增包含示例的笔记本。
- 2024 年 12 月 12 日:上传了用于微调的额外数据集至 [
数据]。增加了随机旋转增强功能。 - 2024 年 12 月 5 日:优化了 target_dist.json 文件的加载流程,改为从 HuggingFace 自动下载。
- 2024 年 12 月 3 日:新增了推理笔记本示例,分别位于 inference_example_RGB.ipynb 和 inference_example_NIFTI.ipynb。
- 2024 年 11 月 22 日:在 inference_example_DICOM.ipynb 中添加了负预测 p 值示例。
- 2024 年 11 月 18 日:BiomedParse 正式发表于 Nature Methods!
安装说明
git clone https://github.com/microsoft/BiomedParse.git
Conda 环境搭建
conda create -n biomedparse_v2 python=3.10.14
conda activate biomedparse_v2
安装依赖项:
pip install -r assets/requirements/requirements.txt
# 上述要求文件假设您的环境使用 cuda12.4。请根据您的系统/环境相应调整。
pip install azureml-automl-core
pip install opencv-python
pip install git+https://github.com/facebookresearch/detectron2.git
模型权重
我们提供了在 CVPR 2025 文本引导的 3D 分割挑战赛 数据集 上训练的模型权重。使用此版本模型时,请务必注明原挑战赛来源。此外,必要的图像预处理也参考了原始数据集。
方法一:HuggingFace Hub
您可以直接从 HuggingFace Hub 下载预训练模型权重。
首先安装所需包:
pip install huggingface_hub
然后使用 HuggingFace Hub API 下载检查点文件:
from huggingface_hub import hf_hub_download
# 下载检查点文件
file_path = hf_hub_download(
repo_id="microsoft/BiomedParse",
filename="biomedparse_v2.ckpt"
)
print("模型权重已下载至:", file_path)
方法二:命令行直接下载
您也可以使用 wget 或 curl 直接下载文件:
wget https://huggingface.co/microsoft/BiomedParse/resolve/main/biomedparse_v2.ckpt
或
curl -L -o biomedparse_v2.ckpt https://huggingface.co/microsoft/BiomedParse/resolve/main/biomedparse_v2.ckpt
💡 提示: 如果仓库为私有,请先使用以下命令登录 HuggingFace 账号并获取令牌:
huggingface-cli login再尝试下载。
现在您已经准备好使用模型权重了!
模型推理
BiomedParse v2 支持以逐层方式对 3D 体积进行分割,每层周围会编码相邻的 3D 上下文信息,并以 RGB 格式呈现。
推理3D 示例
import numpy as np
import torch
import torch.nn.functional as F
import hydra
from hydra import compose
from hydra.core.global_hydra import GlobalHydra
from utils import process_input, process_output, slice_nms
from inference import postprocess, merge_multiclass_masks
from skimage import segmentation
from huggingface_hub import hf_hub_download
device = torch.device("cuda" if torch.cuda.is_available() else "cpu")
print("使用设备:", device)
GlobalHydra.instance().clear()
hydra.initialize(config_path="configs/model", job_name="example_prediction")
cfg = compose(config_name="biomedparse_3D")
model = hydra.utils.instantiate(cfg, _convert_="object")
model.load_pretrained(hf_hub_download(
repo_id="microsoft/BiomedParse", filename="biomedparse_v2.ckpt"))
model = model.to(device).eval()
# 示例图像和提示
file_path = "examples/imgs/CT_AMOS_amos_0018.npz"
npz_data = np.load(file_path, allow_pickle=True)
imgs = npz_data["imgs"]
text_prompts = npz_data["text_prompts"].item()
print("加载的图像形状:", imgs.shape)
print("文本提示:", text_prompts)
ids = [int(_) for _ in text_prompts.keys() if _ != "instance_label"]
ids.sort()
text = "[SEP]".join([text_prompts[str(i)] for i in ids])
imgs, pad_width, padded_size, valid_axis = process_input(imgs, 512)
imgs = imgs.to(device).int()
input_tensor = {
"image": imgs.unsqueeze(0), # 添加批次维度
"text": [text],
}
with torch.no_grad():
output = model(input_tensor, mode="eval", slice_batch_size=4)
mask_preds = output["predictions"]["pred_gmasks"]
mask_preds = F.interpolate(mask_preds, size=(512, 512), mode="bicubic", align_corners=False, antialias=True)
mask_preds = postprocess(mask_preds, output["predictions"]["object_existence"])
mask_preds = merge_multiclass_masks(mask_preds, ids)
mask_preds = process_output(mask_preds, pad_width, padded_size, valid_axis)
print("处理后的掩码形状:", mask_preds.shape)
更多示例请参阅 推理笔记本。
评估
您需要在 <YOUR MODEL AND DATA DIR> 下准备公开模型检查点和评估数据,并将其放入 evaluate_biomedparse.yaml 中,如下所示:
mounts:
external: <YOUR MODEL AND DATA DIR>
将模型检查点保存在 <YOUR MODEL AND DATA DIR> 下。下载 CVPR 2025 文本引导 3D 分割挑战赛的验证集 dataset。将 验证图像 保存到 <YOUR MODEL AND DATA DIR>/data/test 目录下,将 验证掩码 保存到 <YOUR MODEL AND DATA DIR>/data/test_mask 目录下。然后运行以下命令:
python -m azureml.acft.image.components.olympus.app.main \
--config-path <YOUR ABSOLUTE CONFIG DIRECTORY PATH> \
--config-name evaluate_biomedparse
微调
想为您的特定任务提升性能吗?以下是关于在您自己的数据上进行端到端微调的详细说明:FINETUNING
推荐预处理(重要!)
BiomedParse v2 的训练涵盖了五种常用的 3D 生物医学图像模态:CT、MR、PET、超声和显微镜。为了获得合理的性能,务必对推理图像进行与模型训练时相同的预处理。请将所有图像处理成 npz 格式,且强度范围为 [0, 255]。具体来说,对于 CT 图像,请根据部位/解剖结构使用典型的窗宽和窗位值归一化 Hounsfield 单位:
- 软组织(W:400, L:40)
- 肺(W:1500, L:-160)
- 脑(W:80, L:40)
- 骨骼(W:1800, L:400)。
对于其他所有图像,将强度值裁剪到第 0.5 百分位数和第 99.5 百分位数之间。最后,将强度值重新缩放到 [0, 255] 范围内。如果原始强度范围已在 [0, 255] 之内,则无需进行任何预处理。
支持的任务
- CT:肿瘤学/病理学(肾上腺皮质癌、左右肾病变/囊肿、肝脏肿瘤、肺部病变、胰腺肿瘤、头颈部癌症、结肠癌原发灶、COVID-19、全身性病变、淋巴结);胸部(左右肺、左上叶/左下叶/右上叶/右中叶/右下叶、气管、气道树);腹部/盆腔(脾脏、肝脏、胆囊、胃、胰腺、十二指肠、小肠、结肠、食管);泌尿生殖系统/内分泌系统(左右肾、左右肾上腺、膀胱、前列腺、子宫);血管系统(主动脉/分支、上腔静脉、下腔静脉、肺静脉、头臂干、左右锁骨下动脉/颈动脉、左右头臂静脉、左心耳、门静脉/脾静脉、左右髂动脉/静脉);心脏(心脏);头颈部(左右颈动脉、左右下颌下腺/腮腺/泪腺、甲状腺、喉部声门区/声门上区、嘴唇、颊黏膜、口腔、颈段食管、环咽肌入口、杓状软骨、左右眼球前后节、视交叉、左右视神经、左右耳蜗、垂体、脑干、脊髓);神经/颅脑(大脑、颅骨、Willis环CTA);脊柱/肌肉骨骼系统(骶骨、C1–S1椎体、左右肱骨/肩胛骨/锁骨、左右股骨/髋关节、左右臀大肌/中肌/小肌、左右固有肌、左右髂腰肌)。
- MRI:腹部/盆腔(脾脏、肝脏、胆囊、胃、胰腺、十二指肠、小肠全段、结肠全段、食管、膀胱、前列腺、子宫);结肠各段(盲肠、阑尾、升结肠、横结肠、降结肠、乙状结肠、直肠);泌尿生殖系统(前列腺移行带、前列腺病灶);心脏CMR(左心室、右心室、心肌、左心房、右心房);胸部(左右肺);血管系统(主动脉、肺动脉、上腔静脉、下腔静脉、门静脉/脾静脉、左右髂动脉/静脉、左右颈动脉、左右颈内静脉);神经肿瘤/缺血(大脑、脑肿瘤、脑卒中病灶、GTVp/GTVn肿瘤、鼓室内/外的前庭神经鞘瘤、左右耳蜗);胶质瘤成分(非增强肿瘤核心、FLAIR高信号非增强区域、增强组织、切除腔);白质病变(FLAIR/T1高信号白质病变);神经血管(Willis环MRA);脊柱/肌肉骨骼系统(骶骨、局部椎体、椎间盘、椎管/脊髓、左右肱骨/股骨/髋关节、左右臀大肌/中肌/小肌、左右固有肌、左右髂腰肌)。
- 超声:心脏(左心室、心肌、左心房)、颈部(甲状腺、颈动脉、颈内静脉)、神经(脑肿瘤)、小腿肌肉骨骼系统(比目鱼肌、腓肠肌内侧/外侧)。
- PET:全身性病变。
- 电子显微镜:内溶酶体、线粒体、细胞核、神经元超微结构、突触间隙、轴突。
- 光片显微镜:大脑神经活动、阿尔茨海默病斑块、细胞核、血管。
常见问题
相似工具推荐
openclaw
OpenClaw 是一款专为个人打造的本地化 AI 助手,旨在让你在自己的设备上拥有完全可控的智能伙伴。它打破了传统 AI 助手局限于特定网页或应用的束缚,能够直接接入你日常使用的各类通讯渠道,包括微信、WhatsApp、Telegram、Discord、iMessage 等数十种平台。无论你在哪个聊天软件中发送消息,OpenClaw 都能即时响应,甚至支持在 macOS、iOS 和 Android 设备上进行语音交互,并提供实时的画布渲染功能供你操控。 这款工具主要解决了用户对数据隐私、响应速度以及“始终在线”体验的需求。通过将 AI 部署在本地,用户无需依赖云端服务即可享受快速、私密的智能辅助,真正实现了“你的数据,你做主”。其独特的技术亮点在于强大的网关架构,将控制平面与核心助手分离,确保跨平台通信的流畅性与扩展性。 OpenClaw 非常适合希望构建个性化工作流的技术爱好者、开发者,以及注重隐私保护且不愿被单一生态绑定的普通用户。只要具备基础的终端操作能力(支持 macOS、Linux 及 Windows WSL2),即可通过简单的命令行引导完成部署。如果你渴望拥有一个懂你
stable-diffusion-webui
stable-diffusion-webui 是一个基于 Gradio 构建的网页版操作界面,旨在让用户能够轻松地在本地运行和使用强大的 Stable Diffusion 图像生成模型。它解决了原始模型依赖命令行、操作门槛高且功能分散的痛点,将复杂的 AI 绘图流程整合进一个直观易用的图形化平台。 无论是希望快速上手的普通创作者、需要精细控制画面细节的设计师,还是想要深入探索模型潜力的开发者与研究人员,都能从中获益。其核心亮点在于极高的功能丰富度:不仅支持文生图、图生图、局部重绘(Inpainting)和外绘(Outpainting)等基础模式,还独创了注意力机制调整、提示词矩阵、负向提示词以及“高清修复”等高级功能。此外,它内置了 GFPGAN 和 CodeFormer 等人脸修复工具,支持多种神经网络放大算法,并允许用户通过插件系统无限扩展能力。即使是显存有限的设备,stable-diffusion-webui 也提供了相应的优化选项,让高质量的 AI 艺术创作变得触手可及。
ComfyUI
ComfyUI 是一款功能强大且高度模块化的视觉 AI 引擎,专为设计和执行复杂的 Stable Diffusion 图像生成流程而打造。它摒弃了传统的代码编写模式,采用直观的节点式流程图界面,让用户通过连接不同的功能模块即可构建个性化的生成管线。 这一设计巧妙解决了高级 AI 绘图工作流配置复杂、灵活性不足的痛点。用户无需具备编程背景,也能自由组合模型、调整参数并实时预览效果,轻松实现从基础文生图到多步骤高清修复等各类复杂任务。ComfyUI 拥有极佳的兼容性,不仅支持 Windows、macOS 和 Linux 全平台,还广泛适配 NVIDIA、AMD、Intel 及苹果 Silicon 等多种硬件架构,并率先支持 SDXL、Flux、SD3 等前沿模型。 无论是希望深入探索算法潜力的研究人员和开发者,还是追求极致创作自由度的设计师与资深 AI 绘画爱好者,ComfyUI 都能提供强大的支持。其独特的模块化架构允许社区不断扩展新功能,使其成为当前最灵活、生态最丰富的开源扩散模型工具之一,帮助用户将创意高效转化为现实。
gemini-cli
gemini-cli 是一款由谷歌推出的开源 AI 命令行工具,它将强大的 Gemini 大模型能力直接集成到用户的终端环境中。对于习惯在命令行工作的开发者而言,它提供了一条从输入提示词到获取模型响应的最短路径,无需切换窗口即可享受智能辅助。 这款工具主要解决了开发过程中频繁上下文切换的痛点,让用户能在熟悉的终端界面内直接完成代码理解、生成、调试以及自动化运维任务。无论是查询大型代码库、根据草图生成应用,还是执行复杂的 Git 操作,gemini-cli 都能通过自然语言指令高效处理。 它特别适合广大软件工程师、DevOps 人员及技术研究人员使用。其核心亮点包括支持高达 100 万 token 的超长上下文窗口,具备出色的逻辑推理能力;内置 Google 搜索、文件操作及 Shell 命令执行等实用工具;更独特的是,它支持 MCP(模型上下文协议),允许用户灵活扩展自定义集成,连接如图像生成等外部能力。此外,个人谷歌账号即可享受免费的额度支持,且项目基于 Apache 2.0 协议完全开源,是提升终端工作效率的理想助手。
LLMs-from-scratch
LLMs-from-scratch 是一个基于 PyTorch 的开源教育项目,旨在引导用户从零开始一步步构建一个类似 ChatGPT 的大型语言模型(LLM)。它不仅是同名技术著作的官方代码库,更提供了一套完整的实践方案,涵盖模型开发、预训练及微调的全过程。 该项目主要解决了大模型领域“黑盒化”的学习痛点。许多开发者虽能调用现成模型,却难以深入理解其内部架构与训练机制。通过亲手编写每一行核心代码,用户能够透彻掌握 Transformer 架构、注意力机制等关键原理,从而真正理解大模型是如何“思考”的。此外,项目还包含了加载大型预训练权重进行微调的代码,帮助用户将理论知识延伸至实际应用。 LLMs-from-scratch 特别适合希望深入底层原理的 AI 开发者、研究人员以及计算机专业的学生。对于不满足于仅使用 API,而是渴望探究模型构建细节的技术人员而言,这是极佳的学习资源。其独特的技术亮点在于“循序渐进”的教学设计:将复杂的系统工程拆解为清晰的步骤,配合详细的图表与示例,让构建一个虽小但功能完备的大模型变得触手可及。无论你是想夯实理论基础,还是为未来研发更大规模的模型做准备
Deep-Live-Cam
Deep-Live-Cam 是一款专注于实时换脸与视频生成的开源工具,用户仅需一张静态照片,即可通过“一键操作”实现摄像头画面的即时变脸或制作深度伪造视频。它有效解决了传统换脸技术流程繁琐、对硬件配置要求极高以及难以实时预览的痛点,让高质量的数字内容创作变得触手可及。 这款工具不仅适合开发者和技术研究人员探索算法边界,更因其极简的操作逻辑(仅需三步:选脸、选摄像头、启动),广泛适用于普通用户、内容创作者、设计师及直播主播。无论是为了动画角色定制、服装展示模特替换,还是制作趣味短视频和直播互动,Deep-Live-Cam 都能提供流畅的支持。 其核心技术亮点在于强大的实时处理能力,支持口型遮罩(Mouth Mask)以保留使用者原始的嘴部动作,确保表情自然精准;同时具备“人脸映射”功能,可同时对画面中的多个主体应用不同面孔。此外,项目内置了严格的内容安全过滤机制,自动拦截涉及裸露、暴力等不当素材,并倡导用户在获得授权及明确标注的前提下合规使用,体现了技术发展与伦理责任的平衡。