chainer-chemistry
Chainer Chemistry 是一个专为生物与化学领域打造的深度学习库,基于灵活的 Chainer 框架构建。它致力于解决分子数据难以直接应用于传统神经网络的核心难题,帮助研究人员高效预测化合物的各种化学性质。
该工具特别适合从事药物发现、材料科学的研究人员以及需要处理分子结构数据的 AI 开发者使用。其核心亮点在于原生支持图卷积神经网络(GCNN)等前沿模型,能够直接将分子视为图结构数据进行学习,从而更精准地捕捉原子间的复杂关系。此外,Chainer Chemistry 还集成了多种先进的化学信息学算法,并提供了丰富的预置模型,大幅降低了从数据处理到模型训练的门槛。
需要注意的是,使用该库通常需要配合 RDKit 进行分子特征处理,且随着主框架 Chainer 进入维护模式,Chainer Chemistry 目前也主要专注于稳定性维护与关键修复。对于希望深入探索分子深度学习机制、或需要在现有 Chainer 生态中开展生化研究的团队来说,它依然是一个功能扎实、文档详尽的得力助手。
使用场景
某制药公司的 AI 研发团队正致力于从海量化合物库中快速筛选出具有特定抗癌活性的候选分子,以加速新药发现进程。
没有 chainer-chemistry 时
- 研究人员需手动编写复杂的代码将分子结构转换为图数据,并自行实现图卷积神经网络(GCNN)架构,开发周期长达数周。
- 缺乏统一的生物化学数据处理接口,每次实验前都要花费大量时间清洗格式各异的分子描述符和活性标签。
- 难以直接复用学术界最新的分子预测模型,团队不得不重复造轮子,导致算法迭代速度远落后于前沿研究。
- 模型训练过程缺乏针对化学领域的优化,收敛困难且预测准确率不稳定,严重拖慢了虚拟筛选的效率。
使用 chainer-chemistry 后
- 团队直接调用内置的 GCNN 等先进模型接口,仅需几行代码即可完成分子图构建与模型搭建,原型开发缩短至几天内。
- 利用其集成的 RDKit 数据处理管道,自动完成分子标准化、特征提取及数据集划分,大幅减少了预处理的人力投入。
- 轻松加载并微调社区预训练的化学属性预测模型,迅速将最新科研成果转化为实际生产力,提升了模型基线性能。
- 依托专为化学数据优化的深度学习框架,模型训练更加稳定高效,显著提高了对化合物生物活性的预测精度。
chainer-chemistry 通过提供标准化的分子深度学习基础设施,让研发团队从繁琐的工程实现中解放出来,专注于核心药物发现逻辑的创新。
运行环境要求
未说明
未说明
快速开始
Chainer Chemistry:用于生物和化学领域的深度学习库
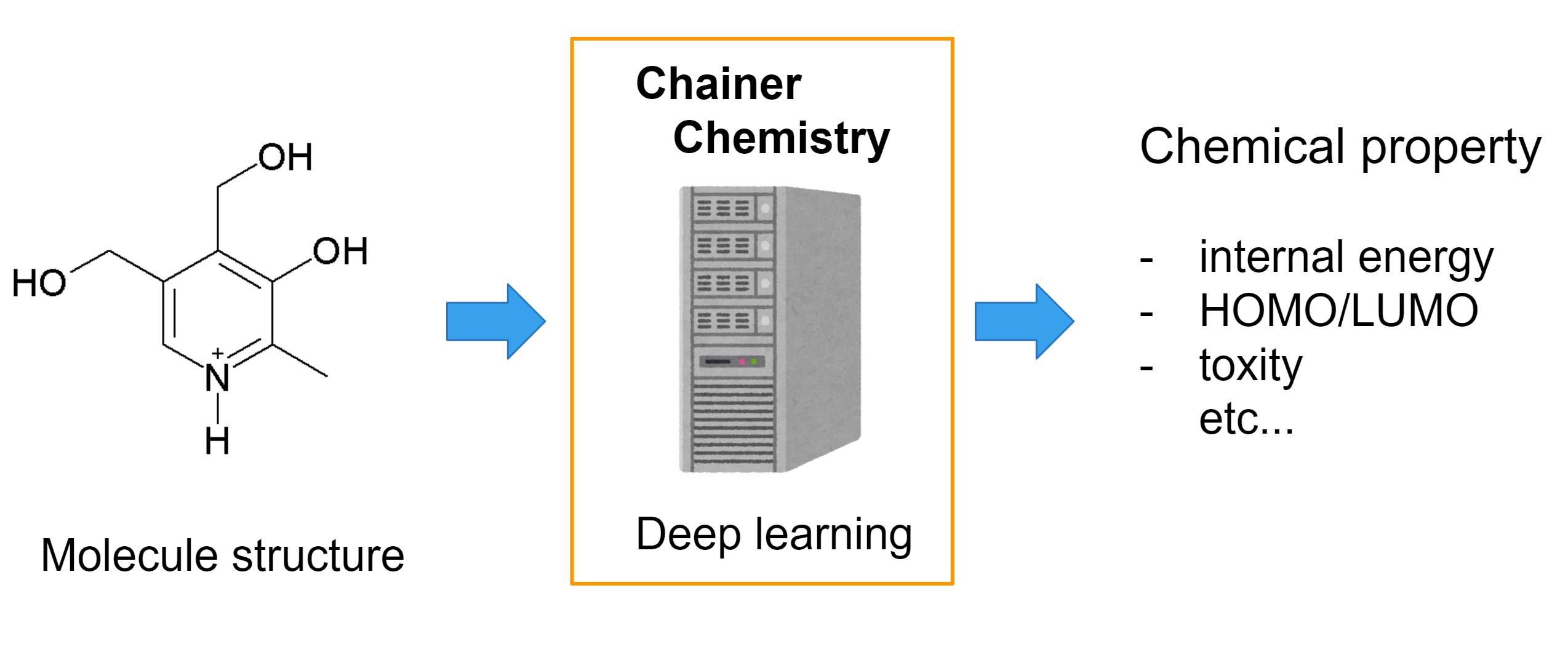
Chainer Chemistry 是一个基于 Chainer 的深度学习框架,专为生物学和化学领域设计。它支持多种最先进的模型(尤其是 GCNN——图卷积神经网络),用于化学性质预测。
如需更多信息,请参阅 文档。此外,关于分子深度学习及 Chainer Chemistry 的简要介绍也可在此处找到:这里。
依赖项
Chainer Chemistry 依赖于以下软件包:
这些依赖项在通过 pip 命令安装该库时会自动添加到系统中(参见“安装”部分)。然而,以下内容需要手动安装:
有关安装步骤的详细信息,请参阅 RDKit 的 文档。
请注意,目前仅支持以下版本的 Chainer Chemistry 依赖项:
| Chainer Chemistry | Chainer | RDKit | Python |
|---|---|---|---|
| v0.1.0 ~ v0.3.0 | v2.0 ~ v3.0 | 2017.09.3.0 | 2.7, 3.5, 3.6 |
| v0.4.0 | v3.0 ~ v4.0 *1 | 2017.09.3.0 | 2.7, 3.5, 3.6 |
| v0.5.0 | v3.0 ~ v5.0 *2 | 2017.09.3.0 | 2.7, 3.5, 3.6 |
| v0.6.0 | v6.0 ~ *3 | 2017.09.3.0 | 2.7, 3.5, 3.6 |
| v0.7.0 ~ v0.7.1 | v7.0 ~ | 2019.03.2.0 | 3.6, 3.7 *4 |
| 主分支 *5 | v7.0 ~ | 2019.03.2.0 | 3.6, 3.7 |
[脚注]
*1:我们在 此 PR 中使用了 FunctionNode,该功能是在 Chainer v3 之后引入的。详情请参阅 此问题。
*2:显著性模块仅在 Chainer v5 及以上版本中可用。
*3:Chainer v6 已发布,并新引入了 ChainerX(https://chainer.org/announcement/2018/12/03/chainerx.html)。为了支持这一新特性和 API,我们对 Chainer Chemistry v0.6.0 版本进行了不兼容的更新。详情请参阅 ChainerX 文档。
*4:根据与 chainer 和 rdkit 相同的政策,不再支持 Python 2.x。
*5:正如 Chainer 官方博客宣布,后续开发将仅限于严重的错误修复和维护工作。
安装
Chainer Chemistry 可以通过以下 pip 命令进行安装:
pip install chainer-chemistry
使用 conda 安装 rdkit 的示例:
# 需要较新的 conda 版本才能安装 rdkit 2019.03.2.0
conda install -n base conda==4.6.14
conda install -c rdkit rdkit==2019.03.2.0
如果您希望使用最新源代码,请检出主分支并使用以下命令进行安装:
git clone https://github.com/pfnet-research/chainer-chemistry.git
pip install -e chainer-chemistry
示例代码
本仓库提供了示例代码,其中包括但不限于以下内容:
- 在给定数据集上训练新模型
- 使用预训练模型对给定数据集进行推理
- 对不同模型在给定数据集上的性能指标进行评估和报告
更多信息请参阅 examples 目录。
支持的模型
目前支持以下图卷积神经网络:
- NFP:神经指纹 [2, 3]
- GGNN:门控图神经网络 [4, 3]
- WeaveNet [5, 3]
- SchNet [6]
- RSGCN:归一化谱图卷积网络 [10]
* 该名称并非源自原始论文——命名规范请参阅 PR #89。 - RelGCN:关系图卷积网络 [14]
- GAT:图注意力网络 [15]
- GIN:图同构网络 [17]
- MPNN:消息传递神经网络 [3]
- Set2Set [19]
- GNN-FiLM:特征线性调制的图神经网络 [20]
- MEGNet:材料图网络 [24]
- CGCNN:晶体图卷积神经网络 [25]
我们正在测试支持全新图扭曲模块(GWM)[18]的以下模型:
- NFP('nfp_gwm')
- GGNN('ggnn_gwm')
- RSGCN('rsgcn_gwm')
- GIN('gin_gwm')
在 examples/molnet_wle 目录中,我们为几种 GNN 架构实现了新的预处理方法“分子图神经网络的魏斯费勒-莱曼嵌入”[26]。请参阅该目录中的 README 文件以获取使用说明和详细信息。
支持的数据集
目前支持以下数据集:
化学类
- QM9 [7, 8]
- Tox21 [9]
- MoleculeNet [11]
- ZINC(仅 25 万数据集)[12, 13]
- 用户自定义数据集
网络类
- cora [21]
- citeseer [22]
- reddit [23]
研究项目
如果您在研究中使用了 Chainer Chemistry,请随时提交拉取请求,并将您的项目名称添加到此列表中:
- BayesGrad:解释图卷积神经网络的预测结果(论文, 代码)
- 图扭曲模块:用于提升图神经网络性能的辅助模块(论文, 代码)
- GraphNVP:用于生成分子图的可逆流模型(论文, 代码)
- 用于分子图生成的图残差流(论文)
有用链接
Chainer Chemistry:
其他 Chainer 框架:
- Chainer:用于深度学习的灵活神经网络框架
- ChainerRL:基于 Chainer 构建的深度强化学习库
- ChainerCV:计算机视觉领域深度学习的库
- ChainerMN:使用 Chainer 实现可扩展的分布式深度学习
- ChainerUI:Chainer 的用户界面
许可证
本项目采用 MIT 许可证发布。更多信息请参阅 此页面。
请注意,Chainer Chemistry 目前仍处于实验性开发阶段。我们不断努力改进其功能和性能,但在现阶段无法保证论文中所发表结果的可重复性。请自行承担使用该库的风险。
参考文献
[1] Seiya Tokui, Kenta Oono, Shohei Hido, and Justin Clayton. Chainer: a next-generation open source framework for deep learning. In Proceedings of Workshop on Machine Learning Systems (LearningSys) in Advances in Neural Information Processing System (NIPS) 28, 2015.
[2] David K Duvenaud, Dougal Maclaurin, Jorge Iparraguirre, Rafael Bombarell, Timothy Hirzel, Alan Aspuru-Guzik, and Ryan P Adams. Convolutional networks on graphs for learning molecular fingerprints. In C. Cortes, N. D. Lawrence, D. D. Lee, M. Sugiyama, and R. Garnett, editors, Advances in Neural Information Processing Systems (NIPS) 28, pages 2224–2232. Curran Asso- ciates, Inc., 2015.
[3] Justin Gilmer, Samuel S Schoenholz, Patrick F Riley, Oriol Vinyals, and George E Dahl. Neural message passing for quantum chemistry. arXiv preprint arXiv:1704.01212, 2017.
[4] Yujia Li, Daniel Tarlow, Marc Brockschmidt, and Richard Zemel. Gated graph sequence neural networks. arXiv preprint arXiv:1511.05493, 2015.
[5] Steven Kearnes, Kevin McCloskey, Marc Berndl, Vijay Pande, and Patrick Riley. Molecular graph convolutions: moving beyond fingerprints. Journal of computer-aided molecular design, 30(8):595–608, 2016.
[6] Kristof Schütt, Pieter-Jan Kindermans, Huziel Enoc Sauceda Felix, Stefan Chmiela, Alexandre Tkatchenko, and Klaus-Rober Müller. Schnet: A continuous-filter convolutional neural network for modeling quantum interactions. In I. Guyon, U. V. Luxburg, S. Bengio, H. Wallach, R. Fergus, S. Vishwanathan, and R. Garnett, editors, Advances in Neural Information Processing Systems (NIPS) 30, pages 992–1002. Curran Associates, Inc., 2017.
[7] Lars Ruddigkeit, Ruud Van Deursen, Lorenz C Blum, and Jean-Louis Reymond. Enumeration of 166 billion organic small molecules in the chemical universe database gdb-17. Journal of chemical information and modeling, 52(11):2864–2875, 2012.
[8] Raghunathan Ramakrishnan, Pavlo O Dral, Matthias Rupp, and O Anatole Von Lilienfeld. Quantum chemistry structures and properties of 134 kilo molecules. Scientific data, 1:140022, 2014.
[9] Ruili Huang, Menghang Xia, Dac-Trung Nguyen, Tongan Zhao, Srilatha Sakamuru, Jinghua Zhao, Sampada A Shahane, Anna Rossoshek, and Anton Simeonov. Tox21challenge to build predictive models of nuclear receptor and stress response pathways as mediated by exposure to environmental chemicals and drugs. Frontiers in Environmental Science, 3:85, 2016.
[10] Kipf, Thomas N. and Welling, Max. Semi-Supervised Classification with Graph Convolutional Networks. International Conference on Learning Representations (ICLR), 2017.
[11] Zhenqin Wu, Bharath Ramsundar, Evan N. Feinberg, Joseph Gomes, Caleb Geniesse, Aneesh S. Pappu, Karl Leswing, Vijay Pande, MoleculeNet: A Benchmark for Molecular Machine Learning, arXiv preprint, arXiv: 1703.00564, 2017.
[12] J. J. Irwin, T. Sterling, M. M. Mysinger, E. S. Bolstad, and R. G. Coleman. Zinc: a free tool to discover chemistry for biology. Journal of chemical information and modeling, 52(7):1757–1768, 2012.
[13] 预处理过的 CSV 文件,下载自 https://raw.githubusercontent.com/aspuru-guzik-group/chemical_vae/master/models/zinc_properties/250k_rndm_zinc_drugs_clean_3.csv
[14] Michael Schlichtkrull, Thomas N. Kipf, Peter Bloem, Rianne van den Berg, Ivan Titov, Max Welling. Modeling Relational Data with Graph Convolutional Networks. Extended Semantic Web Conference (ESWC), 2018。
[15] Veličković, P., Cucurull, G., Casanova, A., Romero, A., Liò, P., & Bengio, Y. (2017). Graph Attention Networks. arXiv preprint arXiv:1710.10903。
[16] Dan Busbridge, Dane Sherburn, Pietro Cavallo and Nils Y. Hammerla. (2019). Relational Graph Attention Networks. https://openreview.net/forum?id=Bklzkh0qFm
[17] Keyulu Xu, Weihua Hu, Jure Leskovec, Stefanie Jegelka, ``How Powerful are Graph Neural Networks?'', arXiv:1810.00826 [cs.LG], 2018 (to appear at ICLR19)。
[18] K. Ishiguro, S. Maeda, and M. Koyama, ``Graph Warp Module: an Auxiliary Module for Boosting the Power of Graph Neural Networks'', arXiv:1902.01020 [cs.LG], 2019。
[19] Oriol Vinyals, Samy Bengio, Manjunath Kudlur. Order Matters: Sequence to sequence for sets. arXiv preprint arXiv:1511.06391, 2015。
[20] Marc Brockschmidt, ``GNN-FiLM: Graph Neural Networks with Feature-wise Linear Modulation'', arXiv:1906.12192 [cs.ML], 2019。
[21] McCallum, Andrew Kachites and Nigam, Kamal and Rennie, Jason and Seymore, Kristie, Automating the Construction of Internet Portals with Machine Learning. Information Retrieval, 2000。
[22] C. Lee Giles and Kurt D. Bollacker and Steve Lawrence, CiteSeer: An Automatic Citation Indexing System. Proceedings of the Third ACM Conference on Digital Libraries, 1998。
[23] William L. Hamilton and Zhitao Ying and Jure Leskovec, Inductive Representation Learning on Large Graphs. Advances in Neural Information Processing Systems 30: Annual Conference on Neural Information Processing Systems 2017, 4-9 December 2017
[24] Chi Chen, Weike Ye, Yunxing Zuo, Chen Zheng, and Shyue Ping Ong. Graph networks as a universal machine learning framework for molecules and crystals. Chemistry of Materials, 31(9):3564–3572, 2019。
[25] Tian Xie and Jeffrey C Grossman. Crystal graph convolutional neural networks for an accurate and interpretable prediction of material properties. Physical review letters, 120(14):145301, 2018。
[26] Katsuhiko Ishiguro, Kenta Oono, and Kohei Hayashi, "Weisfeiler-Lehman Embedding for Molecular Graph Neural Networks", arXiv: 2006.06909, 2020。论文链接
版本历史
v0.7.12020/08/17v0.7.02019/12/10v0.6.02019/09/11v0.5.02019/02/07v0.4.02018/07/19v0.3.02018/04/24v0.2.02018/03/01v0.1.02017/12/14常见问题
相似工具推荐
stable-diffusion-webui
stable-diffusion-webui 是一个基于 Gradio 构建的网页版操作界面,旨在让用户能够轻松地在本地运行和使用强大的 Stable Diffusion 图像生成模型。它解决了原始模型依赖命令行、操作门槛高且功能分散的痛点,将复杂的 AI 绘图流程整合进一个直观易用的图形化平台。 无论是希望快速上手的普通创作者、需要精细控制画面细节的设计师,还是想要深入探索模型潜力的开发者与研究人员,都能从中获益。其核心亮点在于极高的功能丰富度:不仅支持文生图、图生图、局部重绘(Inpainting)和外绘(Outpainting)等基础模式,还独创了注意力机制调整、提示词矩阵、负向提示词以及“高清修复”等高级功能。此外,它内置了 GFPGAN 和 CodeFormer 等人脸修复工具,支持多种神经网络放大算法,并允许用户通过插件系统无限扩展能力。即使是显存有限的设备,stable-diffusion-webui 也提供了相应的优化选项,让高质量的 AI 艺术创作变得触手可及。
everything-claude-code
everything-claude-code 是一套专为 AI 编程助手(如 Claude Code、Codex、Cursor 等)打造的高性能优化系统。它不仅仅是一组配置文件,而是一个经过长期实战打磨的完整框架,旨在解决 AI 代理在实际开发中面临的效率低下、记忆丢失、安全隐患及缺乏持续学习能力等核心痛点。 通过引入技能模块化、直觉增强、记忆持久化机制以及内置的安全扫描功能,everything-claude-code 能显著提升 AI 在复杂任务中的表现,帮助开发者构建更稳定、更智能的生产级 AI 代理。其独特的“研究优先”开发理念和针对 Token 消耗的优化策略,使得模型响应更快、成本更低,同时有效防御潜在的攻击向量。 这套工具特别适合软件开发者、AI 研究人员以及希望深度定制 AI 工作流的技术团队使用。无论您是在构建大型代码库,还是需要 AI 协助进行安全审计与自动化测试,everything-claude-code 都能提供强大的底层支持。作为一个曾荣获 Anthropic 黑客大奖的开源项目,它融合了多语言支持与丰富的实战钩子(hooks),让 AI 真正成长为懂上
ComfyUI
ComfyUI 是一款功能强大且高度模块化的视觉 AI 引擎,专为设计和执行复杂的 Stable Diffusion 图像生成流程而打造。它摒弃了传统的代码编写模式,采用直观的节点式流程图界面,让用户通过连接不同的功能模块即可构建个性化的生成管线。 这一设计巧妙解决了高级 AI 绘图工作流配置复杂、灵活性不足的痛点。用户无需具备编程背景,也能自由组合模型、调整参数并实时预览效果,轻松实现从基础文生图到多步骤高清修复等各类复杂任务。ComfyUI 拥有极佳的兼容性,不仅支持 Windows、macOS 和 Linux 全平台,还广泛适配 NVIDIA、AMD、Intel 及苹果 Silicon 等多种硬件架构,并率先支持 SDXL、Flux、SD3 等前沿模型。 无论是希望深入探索算法潜力的研究人员和开发者,还是追求极致创作自由度的设计师与资深 AI 绘画爱好者,ComfyUI 都能提供强大的支持。其独特的模块化架构允许社区不断扩展新功能,使其成为当前最灵活、生态最丰富的开源扩散模型工具之一,帮助用户将创意高效转化为现实。
NextChat
NextChat 是一款轻量且极速的 AI 助手,旨在为用户提供流畅、跨平台的大模型交互体验。它完美解决了用户在多设备间切换时难以保持对话连续性,以及面对众多 AI 模型不知如何统一管理的痛点。无论是日常办公、学习辅助还是创意激发,NextChat 都能让用户随时随地通过网页、iOS、Android、Windows、MacOS 或 Linux 端无缝接入智能服务。 这款工具非常适合普通用户、学生、职场人士以及需要私有化部署的企业团队使用。对于开发者而言,它也提供了便捷的自托管方案,支持一键部署到 Vercel 或 Zeabur 等平台。 NextChat 的核心亮点在于其广泛的模型兼容性,原生支持 Claude、DeepSeek、GPT-4 及 Gemini Pro 等主流大模型,让用户在一个界面即可自由切换不同 AI 能力。此外,它还率先支持 MCP(Model Context Protocol)协议,增强了上下文处理能力。针对企业用户,NextChat 提供专业版解决方案,具备品牌定制、细粒度权限控制、内部知识库整合及安全审计等功能,满足公司对数据隐私和个性化管理的高标准要求。
ML-For-Beginners
ML-For-Beginners 是由微软推出的一套系统化机器学习入门课程,旨在帮助零基础用户轻松掌握经典机器学习知识。这套课程将学习路径规划为 12 周,包含 26 节精炼课程和 52 道配套测验,内容涵盖从基础概念到实际应用的完整流程,有效解决了初学者面对庞大知识体系时无从下手、缺乏结构化指导的痛点。 无论是希望转型的开发者、需要补充算法背景的研究人员,还是对人工智能充满好奇的普通爱好者,都能从中受益。课程不仅提供了清晰的理论讲解,还强调动手实践,让用户在循序渐进中建立扎实的技能基础。其独特的亮点在于强大的多语言支持,通过自动化机制提供了包括简体中文在内的 50 多种语言版本,极大地降低了全球不同背景用户的学习门槛。此外,项目采用开源协作模式,社区活跃且内容持续更新,确保学习者能获取前沿且准确的技术资讯。如果你正寻找一条清晰、友好且专业的机器学习入门之路,ML-For-Beginners 将是理想的起点。
ragflow
RAGFlow 是一款领先的开源检索增强生成(RAG)引擎,旨在为大语言模型构建更精准、可靠的上下文层。它巧妙地将前沿的 RAG 技术与智能体(Agent)能力相结合,不仅支持从各类文档中高效提取知识,还能让模型基于这些知识进行逻辑推理和任务执行。 在大模型应用中,幻觉问题和知识滞后是常见痛点。RAGFlow 通过深度解析复杂文档结构(如表格、图表及混合排版),显著提升了信息检索的准确度,从而有效减少模型“胡编乱造”的现象,确保回答既有据可依又具备时效性。其内置的智能体机制更进一步,使系统不仅能回答问题,还能自主规划步骤解决复杂问题。 这款工具特别适合开发者、企业技术团队以及 AI 研究人员使用。无论是希望快速搭建私有知识库问答系统,还是致力于探索大模型在垂直领域落地的创新者,都能从中受益。RAGFlow 提供了可视化的工作流编排界面和灵活的 API 接口,既降低了非算法背景用户的上手门槛,也满足了专业开发者对系统深度定制的需求。作为基于 Apache 2.0 协议开源的项目,它正成为连接通用大模型与行业专有知识之间的重要桥梁。



